Science:粘连蛋白在DNA修复中引导同源性搜索
来源:生物谷原创 2026-01-04 10:14
Sister-pore-C 能够实现染色单体内部和姐妹染色单体之间接触的全基因组绘图,为探索其他过程(如减数分裂)中的重组架构提供了一个框架。
精确修复DNA双链断裂(DSBs)对于基因组稳定性至关重要,因为错误可能导致细胞死亡或与癌症相关的染色体重排。 同源重组通过从一个完整的模板(通常是姐妹染色单体)复制,来恢复断裂处周围的DNA序列。一个关键的挑战在于理解断裂的DNA末端如何在折叠的基因组内定位正确的同源序列。尽管修复的生化步骤已有详细描述,但核结构对同源性搜索(homology search)过程的贡献仍不清楚。

粘连蛋白(cohesin)是一种环状蛋白质复合物,它通过挤出DNA环形成拓扑关联域(TADs)以及连接姐妹染色单体来组织染色体。这两种功能都会影响基因组拓扑结构,但这如何影响同源性搜索尚不清楚。为了解决这个问题,研究人员开发了sister-pore-C,这是一种在全基因组范围内绘制染色单体内部和染色单体之间接触的高分辨率方法。结合靶向DSB诱导和急性粘连蛋白扰动,该方法使我们能够确定粘连蛋白介导的结构如何在修复过程中指导RAD51丝状结构的采样。
RAD51丝状结构主要在DSB附近和TAD边界内进行同源序列采样,这表明粘连蛋白介导的环控制了搜索空间。丢失具有环挤出功能的粘连蛋白会缩小RAD51的分布范围,而过度活跃的环挤出则会扩大采样范围,但会降低其在DNA断裂附近的局部浓度。Sister-pore-C显示,DSB局部重塑了染色体结构,增加了环化并促进了断裂处附近与姐妹染色单体的接触。粘连蛋白定位显示,具有环挤出功能的复合物在DSB周围一个广泛的区域积累,而具有粘合功能的粘连蛋白则集中在断裂点本身,从而建立了不同的顺式和反式姐妹染色单体架构。从功能上讲,消耗具有环挤出功能的粘连蛋白或过度挤出会延迟修复,而失去粘合功能则会完全中止修复,这表明两种机制对于高效的同源重组都至关重要。
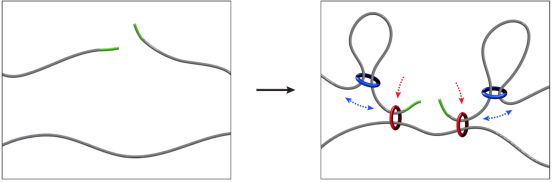
粘连蛋白通过双重机制指导同源性搜索:一个粘合钳将断裂的DNA末端拴系在姐妹染色单体上,而环挤出则控制在局部TAD内的采样。这种空间组织缩小了搜索空间并加速了修复,从而确立了染色体拓扑结构是修复效率的一个主动决定因素。Sister-pore-C 能够实现染色单体内部和姐妹染色单体之间接触的全基因组绘图,为探索其他过程(如减数分裂)中的重组架构提供了一个框架。(生物谷Bioon.com)
参考文献:
Federico Teloni et al, Cohesin guides homology search during DNA repair using loops and sister chromatid linkages, Science (2025). DOI:10.1126/science.adw0566.
版权声明 本网站所有注明“来源:生物谷”或“来源:bioon”的文字、图片和音视频资料,版权均属于生物谷网站所有。非经授权,任何媒体、网站或个人不得转载,否则将追究法律责任。取得书面授权转载时,须注明“来源:生物谷”。其它来源的文章系转载文章,本网所有转载文章系出于传递更多信息之目的,转载内容不代表本站立场。不希望被转载的媒体或个人可与我们联系,我们将立即进行删除处理。


