Nature:清华大学陈柱成/李雪明团队揭示NuA4选择性乙酰化组蛋白H4的机理
来源:生物世界 2022-10-07 13:08
清华大学生命科学学院陈柱成教授与李雪明副教授合作,在
清华大学生命科学学院陈柱成教授与李雪明副教授合作,在 Nature 期刊在线发表题为:Structure of the NuA4 acetyltransferase complex bound to the nucleosome(酿酒酵母NuA4乙酰转移酶复合物结合核小体的结构)的研究论文。
该研究揭示了乙酰转移酶NuA4结合核小体以及组蛋白H4空间识别的机理,阐明了NuA4作为转录共激活因子发挥功能的结构基础。

生物体遗传信息DNA缠绕组蛋白八聚体1.7圈形成了染色体的基本组成单位——核小体。组蛋白H4的 N端尾巴与临近的核小体相互作用,促进染色体高级结构的形成以及异染色质沉默。核小体组装和异染色质形成阻碍了DNA的复制、转录以及损伤修复等重要生物学过程。
生物体进化出了一系列的机制来克服核小体的阻碍。其中,组蛋白乙酰化修饰中和赖氨酸侧链的正电荷,并招募其他染色质因子,进而调控染色质折叠、基因转录以及DNA损伤修复等过程。
NuA4和SAGA是酿酒酵母两个重要的乙酰转移酶复合物,分别选择性地乙酰化组蛋白H4和H3,调控基因转录。NuA4和SAGA在不同物种中高度保守,前者是酵母生存唯一必需的乙酰转移酶。作为转录共激活因子,二者通过共同亚基Tra1,结合转录因子,被招募至启动子区(图1a)。因为有基础性作用,NuA4自发现至今20多年被不断研究,但其结构研究历史相当曲折,目前尚不清楚精细的分子组装模式以及识别底物核小体的机理。
图1 NuA4的工作模式图及结合核小体的结构。(a)NuA4与SAGA协同作用促进基因转录的工作模式图;(b)NuA4结合核小体的示意图;(c)NuA4-NCP复合物的电镜密度图。(d)NuA4各亚基结构域组成示意图,颜色与电镜密度图中一致。
陈柱成课题组早期报道了NuA4活性中心Piccolo亚复合物的晶体结构及其结合核小体的低分辨率冷冻电镜结构。在此基础上,研究团队继续向着NuA4全酶的结构解析进击。然而,研究人员发现NuA4复合物的结构可塑性非常大,其活性中心结合核小体的部分无法得到稳定构象。这造成高质量结构解析的关键技术难点。
为了限制复合物结构的柔性,研究团队在样品中加入了转录因子Gal4-VP16,并在核小体接头 DNA引入相应的识别DNA序列,作为上游激活信号(UAS)。而且,研究团队对组蛋白H4K16位点进行CMC(carboxymethyl coenzyme A)化学修饰以及H3K36位点进行三甲基化修饰。CMC结合NuA4的催化中心Esa1,稳定Esa1与核小体的作用;H3K36则结合Eaf3亚基。在突破各种技术难题后,最终解析了NuA4结合核小体的冷冻电镜结构(8.8 Å),局部分辨率为2.7-3.4 Å。
由13个亚基组成的NuA4复合物分为两个大的模块 (图1c, d):乙酰化模块(histone acetyltransferase, HAT)以及转录因子结合模块(transcription activator-binding, TRA)。HAT模块即为piccolo亚复合物,由Esa1、Epl1的N端区域、Eaf6以及Yng2组成;TRA模块则由Tra1、Eaf1、Eaf2、Act1、Arp4以及Epl1的C端区域组成。Epl1的一段无序区把HAT模块与TRA模块连接在一起。另外,还存在一个“桥型”的结构柔性区。研究人员根据交联质谱推断这部分区域为Eaf3/5/7亚基。从这里可以看出NuA4复合物构造的高度可塑性。
该结构显示,携带UAS的linker DNA延伸向Tra1亚基的特定表面(图2a, b)。有趣的是,研究人员发现该表面在不同物种中高度保守,且众多转录因子与Tra1的结合位点均位于该表面内。因此,该保守面被命名为转录因子结合面(transcription factor binding surface, ABS)。这个发现提供了NuA4被转录因子招募至启动子区域的结构基础。
在ABS外周,研究人员发现一个多碱性氨基酸界面(poly-basic surface, PBS)与核小体的linker DNA相互作用(图2c)。研究人员通过体外生化以及遗传学实验验证了PBS的对乙酰转移活性,以及调控酵母碳源代谢的重要性(图2d, e)。
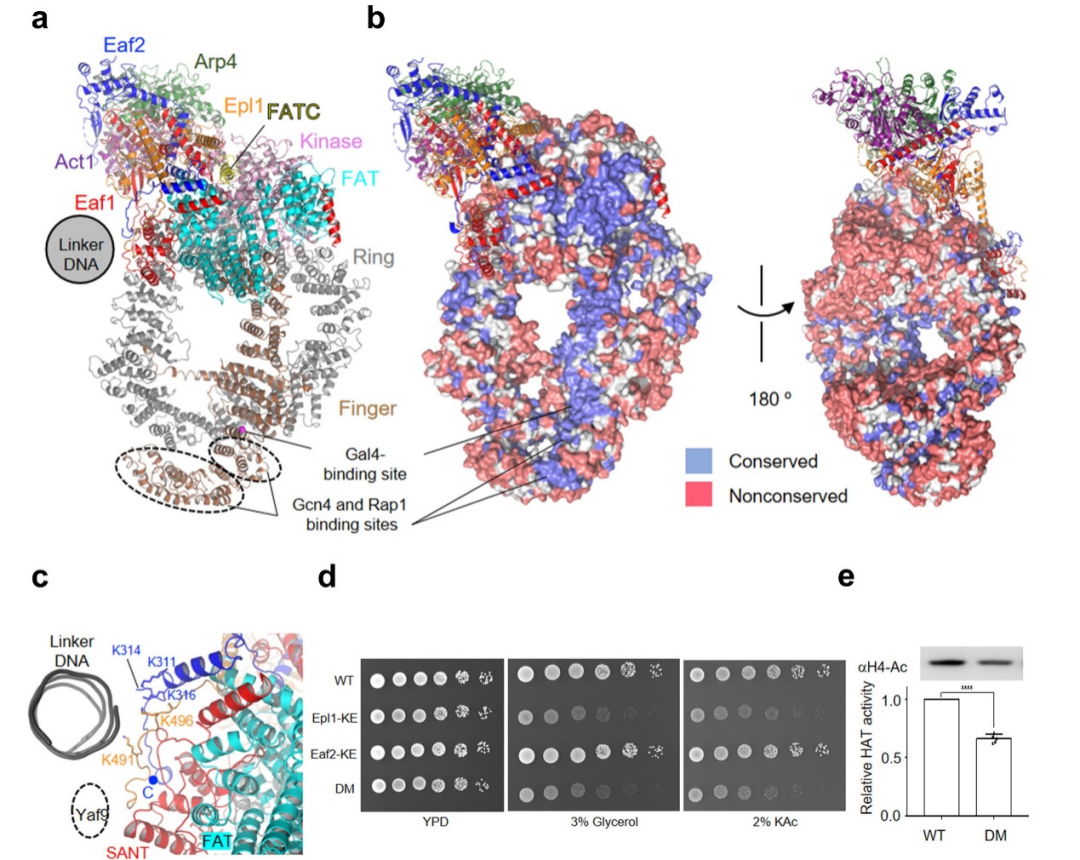 图2:NuA4的 TRA模块结构和核小体识别机理。(a)TRA模块的结构模型;(b)转录因子结合表面(ABS)的保守性;(c)多碱性氨基酸结合表面(PBS)的结构细节;(d)酵母遗传学实验显示PBS对NuA4发挥功能的重要性;(e)体外乙酰转移酶活性实验显示PBS对NuA4乙酰化活性的重要性。
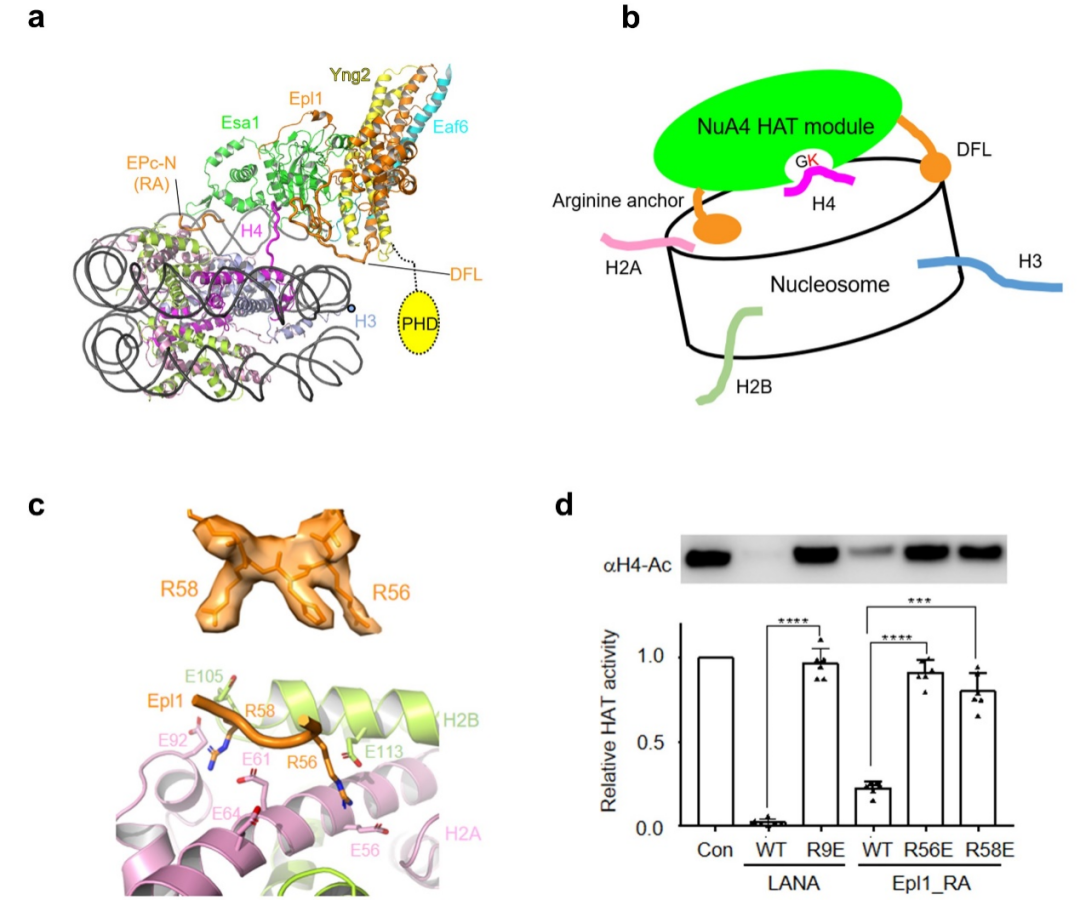
催化中心HAT模块通过两个关键元件识别核小体的特定位点,结合在核小体盘状结构表面。其中Epl1的“arginine anchor”识别核小体的酸性区, 一段“double function loop (DFL)”识别核小体的超螺旋1.5(SHL 1.5)位置处DNA的小沟(图3a, c, d)。该核小体识别模式使得Esa1的活性口袋恰好处在H4 的N端尾巴上方。这个结构在全酶水平支持了H4尾巴空间位置识别机制(图3b)。该机制区别于常见的基于氨基酸序列识别的组蛋白修饰酶工作机制。
综上所述,该研究揭示了NuA4通过多个结构元件,协调识别核小体的机理(图1b)。ABS通过转录因子,PBS直接结合接头DNA,招募核小体至TRA模块的边缘;在此构象下使得HAT模块通过DFL和arginine anchor识别核小体的表面位点,从而发挥选择性乙酰化H4的功能。TRA模块与HAT模块之间的可塑性,使得NuA4能够适应复杂的染色体环境中被不同转录因子招募。除了Eaf5亚基之外,其他亚基在人源TIP60复合物中均存在同源蛋白。因此,该研究对于理解TIP60复合物的组装及工作机制提供了很好的模型。
值得一提的是,该工作TRA模块的结构被另外三个单独的NuA4复合物的结构研究所验证(预印版,见延伸阅读)。
图3 NuA4 HAT模块识别核小体的机理。(a)HAT模块结合核小体的结构模型;(b)HAT模块通过空间位置识别H4的模式图;(c)Arginine anchor局部电镜密度图及其与酸性区相互作用结构细节;(d)多肽竞争性实验显示Arginine anchor对NuA4乙酰化活性的重要性。
清华大学生命科学学院陈柱成教授、李雪明副教授为论文共同通讯作者,清华大学生命科学学院2014级博士生瞿珂珂(已毕业)和2017级博士生陈康净(已毕业)、王皓为共同第一作者。
图2:NuA4的 TRA模块结构和核小体识别机理。(a)TRA模块的结构模型;(b)转录因子结合表面(ABS)的保守性;(c)多碱性氨基酸结合表面(PBS)的结构细节;(d)酵母遗传学实验显示PBS对NuA4发挥功能的重要性;(e)体外乙酰转移酶活性实验显示PBS对NuA4乙酰化活性的重要性。
催化中心HAT模块通过两个关键元件识别核小体的特定位点,结合在核小体盘状结构表面。其中Epl1的“arginine anchor”识别核小体的酸性区, 一段“double function loop (DFL)”识别核小体的超螺旋1.5(SHL 1.5)位置处DNA的小沟(图3a, c, d)。该核小体识别模式使得Esa1的活性口袋恰好处在H4 的N端尾巴上方。这个结构在全酶水平支持了H4尾巴空间位置识别机制(图3b)。该机制区别于常见的基于氨基酸序列识别的组蛋白修饰酶工作机制。
综上所述,该研究揭示了NuA4通过多个结构元件,协调识别核小体的机理(图1b)。ABS通过转录因子,PBS直接结合接头DNA,招募核小体至TRA模块的边缘;在此构象下使得HAT模块通过DFL和arginine anchor识别核小体的表面位点,从而发挥选择性乙酰化H4的功能。TRA模块与HAT模块之间的可塑性,使得NuA4能够适应复杂的染色体环境中被不同转录因子招募。除了Eaf5亚基之外,其他亚基在人源TIP60复合物中均存在同源蛋白。因此,该研究对于理解TIP60复合物的组装及工作机制提供了很好的模型。
值得一提的是,该工作TRA模块的结构被另外三个单独的NuA4复合物的结构研究所验证(预印版,见延伸阅读)。
图3 NuA4 HAT模块识别核小体的机理。(a)HAT模块结合核小体的结构模型;(b)HAT模块通过空间位置识别H4的模式图;(c)Arginine anchor局部电镜密度图及其与酸性区相互作用结构细节;(d)多肽竞争性实验显示Arginine anchor对NuA4乙酰化活性的重要性。
清华大学生命科学学院陈柱成教授、李雪明副教授为论文共同通讯作者,清华大学生命科学学院2014级博士生瞿珂珂(已毕业)和2017级博士生陈康净(已毕业)、王皓为共同第一作者。
版权声明
本网站所有注明“来源:生物谷”或“来源:bioon”的文字、图片和音视频资料,版权均属于生物谷网站所有。非经授权,任何媒体、网站或个人不得转载,否则将追究法律责任。取得书面授权转载时,须注明“来源:生物谷”。其它来源的文章系转载文章,本网所有转载文章系出于传递更多信息之目的,转载内容不代表本站立场。不希望被转载的媒体或个人可与我们联系,我们将立即进行删除处理。
87%用户都在用生物谷APP 随时阅读、评论、分享交流 请扫描二维码下载->


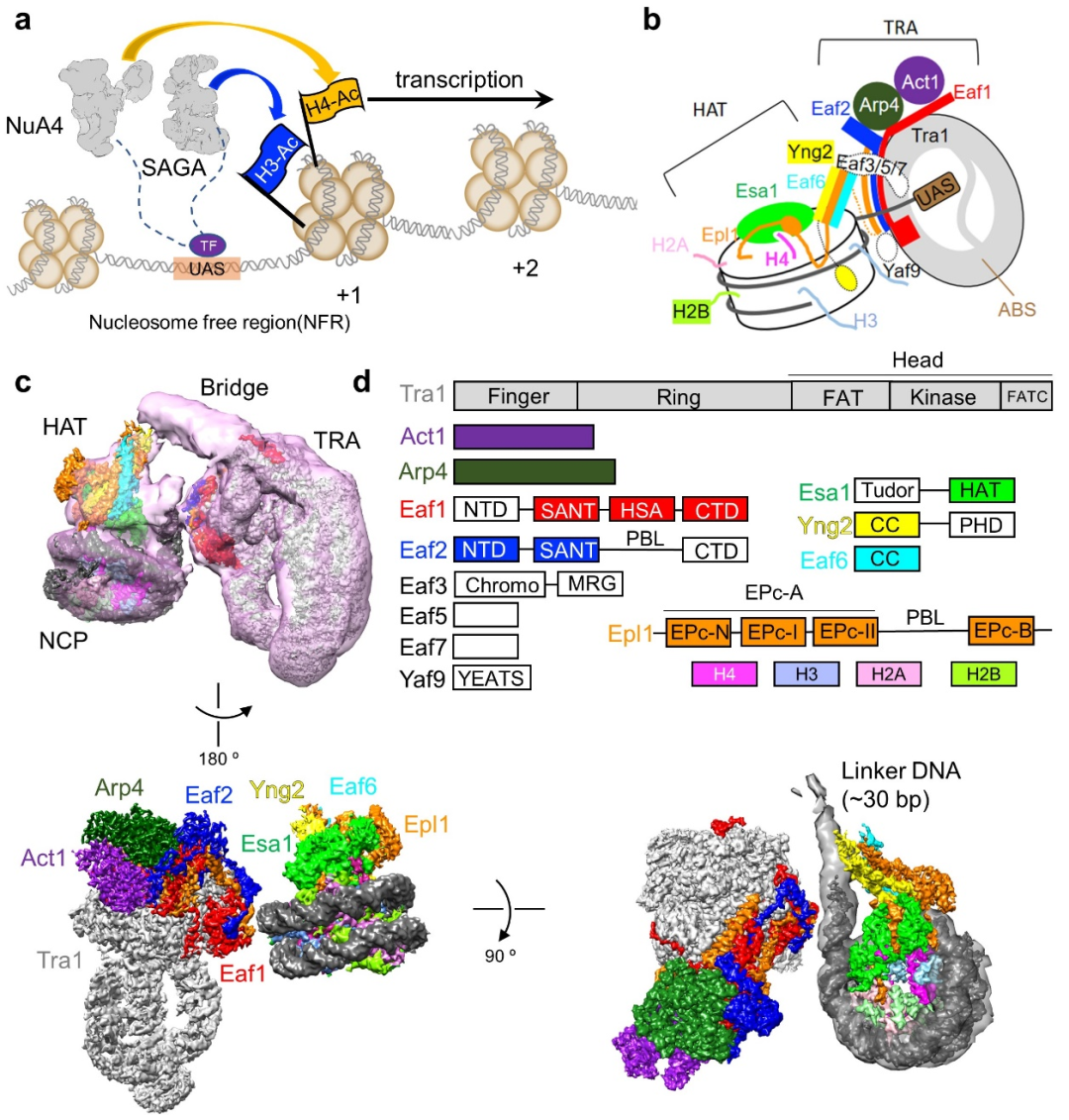
 图2:NuA4的 TRA模块结构和核小体识别机理。(a)TRA模块的结构模型;(b)转录因子结合表面(ABS)的保守性;(c)多碱性氨基酸结合表面(PBS)的结构细节;(d)酵母遗传学实验显示PBS对NuA4发挥功能的重要性;(e)体外乙酰转移酶活性实验显示PBS对NuA4乙酰化活性的重要性。
图2:NuA4的 TRA模块结构和核小体识别机理。(a)TRA模块的结构模型;(b)转录因子结合表面(ABS)的保守性;(c)多碱性氨基酸结合表面(PBS)的结构细节;(d)酵母遗传学实验显示PBS对NuA4发挥功能的重要性;(e)体外乙酰转移酶活性实验显示PBS对NuA4乙酰化活性的重要性。